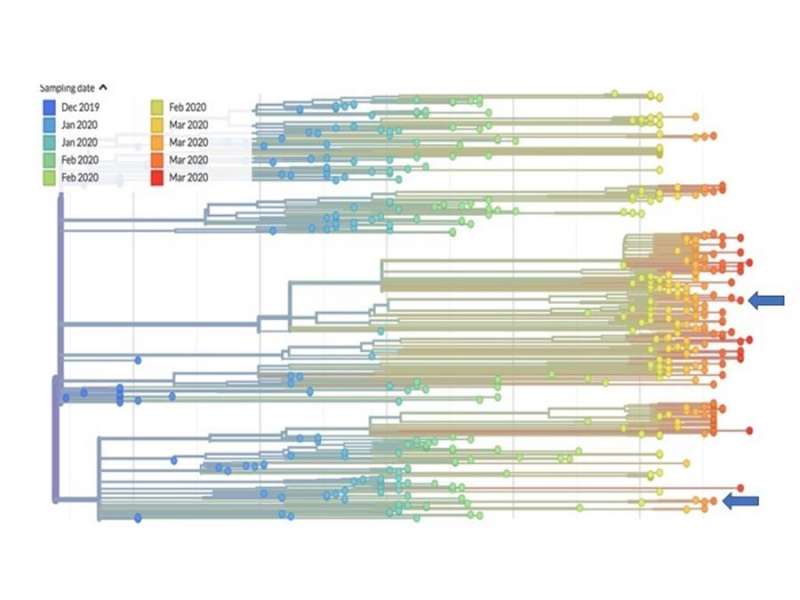
 Filogenia del coronavirus SARS-CoV-2 con las secuencias disponibles en Nextstrain, en un gráfico compartido por la UV. Las flechas señalan los linajes de los virus aislados en València.
Filogenia del coronavirus SARS-CoV-2 con las secuencias disponibles en Nextstrain, en un gráfico compartido por la UV. Las flechas señalan los linajes de los virus aislados en València.La Universitat de València (UV) y la Fundación para el Fomento de la
Investigación Sanitaria y Biomédica de la Comunitat Valenciana (Fisabio)
han obtenido los primeros genomas completos del virus SARS-CoV2 en
España.
La secuenciación del genoma del virus permite conocer las
mutaciones que ha sufrido desde que comenzó la epidemia y la conclusión
a la que se ha llegado después del análisis realizado es que, hasta
ahora, no se ha encontrado ninguna mutación asociada a una mayor
virulencia, letalidad o a alguna propiedad interesante desde el punto de
vista clínico.
Los equipos de investigación valencianos han
conseguido secuenciar el genoma completo de tres muestras de pacientes
infectados por el COVID-19 procedentes del laboratorio de Microbiología
del Hospital Clínico Universitario de València, las primeras secuencias
del virus SARS-CoV2 obtenidas en España.
Según ha informado la UV
en un comunicado, esta secuenciación de genomas completos se suma al
esfuerzo que se está haciendo a nivel mundial en todos los laboratorios
para averiguar cuáles han sido las vías de transmisión y cómo se
extienden los diferentes linajes del virus.
El análisis genómico
ha sido llevado a cabo por la Unidad Mixta en Infección y Salud Pública
de la UV y el Grupo de Investigación en Epidemiología Molecular de
Fisabio, ambos liderados por Fernando González, catedrático de Genética e
investigador, y el Servicio de Secuenciación y Bioinformática de
Fisabio que coordinan Giuseppe d’Auria y Llúcia Martínez.
"El
objetivo primordial es identificar con mayor fiabilidad los focos y las
cadenas de transmisión del coronavirus. La principal conclusión del
análisis de las primeras muestras es que las cepas proceden de rutas de
transmisión diferentes", ha explicado Fernando González.
Los
grupos, formados por personal investigador especialista en virología,
epidemiología y bioinformática, han determinado que una de las cepas
analizadas está relacionada con otras cepas europeas (de Italia,
Alemania, Luxemburgo, Francia, Escocia, Países Bajos...)
"El
siguiente paso será analizar secuencias de más muestras de pacientes de
los hospitales de la Comunitat Valenciana para poder comprobar las
vinculaciones entre ellas y con las cadenas de transmisión establecidas
por el personal especialista en epidemiología", ha señalado González.
El
análisis de genomas virales permite conocer las vías por las cuales ha
entrado el virus a nuestra comunidad y cómo se transmite en estos
momentos, lo que ayudará a las autoridades sanitarias a controlar mucho
mejor la expansión del virus.
Las secuencias ya están accesibles
en la base de datos de la Iniciativa GISAID, consorcio público dedicado
al estudio del virus de la gripe (https://www.gisaid.org/); la
plataforma Nextstrain, que permite visualizar la progresión espacial y
temporal de la pandemia a partir de los más de 500 genomas depositados
desde el pasado diciembre por 40 países (https://nextstrain.org/); y la
base de datos Genbank de secuencias genéticas del National Institutes of
Health (NIH) de Estados Unidos (https://www.ncbi.nlm.nih.gov/genbank).
Las
muestras han sido secuenciadas mediante MinIOn, un secuenciador de
tercera generación de Oxford Nanopore Technologies. La infraestructura
utilizada en la investigación ha sido posible gracias a la
cofinanciación de la Unión Europea a través del Programa Operativo del
Fondo Europeo de Desarrollo Regional (Feder) de la Comunitat Valenciana
2014-2020.
Comparte la noticia
Categorías de la noticia